2013年1月22日
独立行政法人理化学研究所
国立大学法人九州工業大学
未知のゲノム領域にペプチド大陸が存在
-短い遺伝子の中に形態形成に関わるものが高確率で存在することを示唆-
ポイント
- 短い遺伝子領域の同定に特化した手法を開発し7,901個の新規遺伝子を推定
- シロイヌナズナからペプチドをコードする短い遺伝子を7,000個以上発見
- 植物の環境耐性強化や生産性向上につながり、農業分野での貢献が期待
要旨
理化学研究所(野依良治理事長)と九州工業大学(松永守央学長)は、モデル植物であるシロイヌナズナの未知のゲノム領域から、小さなタンパク質であるペプチドをコードする短い遺伝子を、7,000個以上発見しました。さらに、これらの遺伝子の一部は、形態形成に関与することを明らかにしました。これは、理研植物科学研究センター(篠崎一雄センター長)機能開発研究グループの花田耕介客員研究員(九州工業大学若手研究者フロンティア研究アカデミー准教授)、樋口美栄子研究員、植物ゲノム機能研究グループの松井南グループディレクターらの共同研究グループによる成果です。
生命現象を理解するには、全DNA配列(ゲノム)を解読し、かつ個々のDNA配列の機能や役割を検討する必要があります。特に、細胞の主要成分であるタンパク質はアミノ酸が繋がってできているため、アミノ酸配列をコードするDNA配列領域(遺伝子)を同定することが重要です。しかし、これまでアミノ酸配列をコードするのは長い遺伝子と考えられ、短い遺伝子は注目されていませんでした。
共同研究グループは、短い遺伝子の同定のために開発した情報解析を用いて、すでに多くのゲノム解析が行われているシロイヌナズナを調べたところ、これまで注目されていなかったゲノム領域から新規に7,901個の短い遺伝子を推定しました。これら遺伝子が機能するのか確認するため、33の異なる条件下でRNA発現を調べたところ、7,000個以上がRNA発現していることが分かり、「ペプチド大陸」と名付けました。この中から473個を無作為に選び、それらが過剰発現する変異体を作製した結果、約10%にあたる49個の過剰発現体が形態異常を示しました。これまで、網羅的な既知遺伝子の過剰発現解析では、1.4%程度の割合でしか形態形成に関わる遺伝子は発見されていません。それに比べると、今回発見したペプチド大陸には高確率で形態形成に関わる短い遺伝子が存在することが分かりました。
つまり、まだ同定されていない短い遺伝子の中に、形態形成に関係するものが数多く存在することを示唆しています。
また、多数の短い遺伝子を同定する方法を開発したことも成果です。今後、環境耐性などに関わるペプチドが同定されれば、生産性の向上につながり、農業分野に大きな貢献を果たす可能性があります。また、動物でも、数多くの重要な短い遺伝子の存在が予想されます。今後、医療も含めてさまざまな生物の分野に波及すると期待できます。
本研究成果は、農業・食品産業技術総合研究機構生物系特定産業技術研究支援センターのイノベーション創出基礎的研究推進事業、平成21年度採択課題「インシリコ予測に基づいた植物の新規機能性低分子ペプチドの探索」(研究代表者:花田耕介)により主に行われ、米国の科学アカデミー紀要『Proceedings of the National Academy of Sciences of the United States of America(PNAS)』オンライン版に1月21日の週に掲載されます。
背景
全DNA配列(ゲノム)の解読は、生命現象の理解の基盤となるため、さまざまな生物種のゲノムプロジェクトが実施されています。しかし、ゲノム配列を読み取っただけでは生命現象の理解には不十分であり、個々のDNA配列の機能や役割を検討する必要があります。特に、アミノ酸配列をコードする遺伝子は、細胞の主要な構成成分であるタンパク質の種類を決定するため、そのような遺伝子領域を同定することが重要になります。アミノ酸配列情報は、DNAから転写されたRNAの配列情報からなります。そのため、RNAへの転写領域の解読も、ゲノム解読と同時に実施されています。
近年のRNAの網羅的な転写解析によって、これまでタンパク質をコードする遺伝子領域ではないと考えられていた領域にも、RNAに転写される領域が多数存在することが明らかになってきました。こうしたRNA転写領域には、100アミノ酸以下という短いアミノ酸配列から成るペプチドをコードする短い遺伝子があり、近年、さまざまな生物種で、生命の維持に必須な機能があることが明らかとなってきました。そこで、これまでにゲノムの多くが解読され、遺伝子の間隙が短いため機能解析がしやすいモデル植物のシロイヌナズナを用いて、ペプチドをコードする新規の短い遺伝子の同定や、それらの機能解析に挑みました。
研究手法と成果
共同研究グループは、アミノ酸をコードするDNA、RNA配列のパターンを抽出することが可能な機械学習法を開発し、シロイヌナズナを対象に既知遺伝子が存在しないところの短い遺伝子を予測しました(図1)。その結果、未知のゲノム領域から、新規に7,901個の短い遺伝子領域を推定しました。次に、これらの短い遺伝子の候補が、遺伝子として機能しているかを確認するために、マイクロアレイ[1]を作製し、16カ所の組織、9つの異なるストレス条件下、8つの異なる光条件下という合計33の条件下で、RNA発現強度を調べました(図2上)。その結果、弱いRNA発現が7,000個以上ありました。特に、非常に強いRNA発現を2,099個確認し、遺伝子としての機能を見いだしました(図2下)。共同研究グループは、これを「ペプチド大陸」と名付けました。
さらに、7,000個以上の中から473個を無作為に選び、これらがコードするペプチドを過剰発現させた変異体を作製し、観察した結果、約10%にあたる49個の過剰発現体で野生型とは異なる異常な形態を示すことが分かりました(表1)。長い遺伝子を対象とした網羅的な過剰発現解析では、1.4%程度の割合でしか形態形成に関わる遺伝子を発見できないといわれています。今回の結果は、未知のゲノム領域に、形態形成に関係するペプチドをコードする短い遺伝子が数多く存在する可能性を示唆しています。
今回発見した形態形成に関係する49個の遺伝子の機能の詳細を調べるため、それらの遺伝子が発現する組織や条件の全てに共通して発現している既知の遺伝子群を観察しました。その結果、植物ホルモンに関わるペプチド遺伝子が、共発現していることが分りました。これは、今回同定された遺伝子がコードするペプチドが、植物ホルモンに関わることを示唆しています。
今後の期待
33の条件下において、49個の新規の短い遺伝子と既知遺伝子の発現量は、今回構築されたデータベース「HanaDB-AT」で、誰でも自由に利用できます。また、このデータベースでは、新規に推定した短い遺伝子と同じ条件で発現している遺伝子を推定する共発現解析や、ゲノム上の位置を確認するアプリケーションも提供しています。
本研究で発見した短い遺伝子は、シロイヌナズナ以外の植物にも保存されていることも分かりました。そのため、今回発見した「ペプチド大陸」の中から、生産性や環境耐性に関わるものが同定できると、そのペプチドを利用し、バイオマスエネルギー産業や農業分野に大きな貢献を果たす可能性があります。また、動物においても生命維持に関わる数多くの短い遺伝子が存在することが予想され、医療も含めてさまざまな生物分野への展開が期待できます。
原論文情報
- Kousuke Hanada, Mieko Higuchi, Masanori Okamotoa, Takeshi Yoshizumi, Minami Shimizu,Kentaro Nakaminami, Ranko Nishi, Chihiro Ohashi, Kei Iid, Maho Tanaka, Yoko Horii, Mika Kawashima,Keiko Matsui, Tetsuro Toyoda, Kazuo Shinozaki, Motoaki Seki, and Minami Matsui,
"Small open reading frames associated with morphogenesis are hidden in plant genomes".
Proceedings of the National Academy of Sciences of the United States of America(PNAS), doi:10.1073/pnas.1213958110.
発表者
理化学研究所
植物科学研究センター 機能開発研究グループ
客員研究員 花田 耕介(はなだ こうすけ)
国立大学法人九州工業大学
若手研究者フロンティア研究アカデミー 准教授
国立大学法人九州工業大学 若手研究者フロンティア研究アカデミー
准教授 花田 耕介(はなだ こうすけ)
お問い合わせ先
独立行政法人理化学研究所 横浜研究推進部企画課
Tel: 045-503-9117 / Fax: 045-503-9113
報道担当
独立行政法人理化学研究所 広報室 報道担当
Tel:048-467-9272 / Fax:048-462-4715
国立大学法人九州工業大学 総務課 広報企画係
Tel: 093-884-3007 / Fax: 093-884-3015
補足説明
- 1.マイクロアレイ
遺伝子発現量を測定するために、あらかじめ塩基配列の明らかな1本鎖のDNAを基板上に配置する。これに調べたい検体のRNA配列の集団を反応させると、RNA配列と相補的な塩基配列の部分だけ検体のRNA鎖が結合する。この結合位置および強度を蛍光で検出し、検体に含まれるさまざまなRNA量を定量することが可能になる。
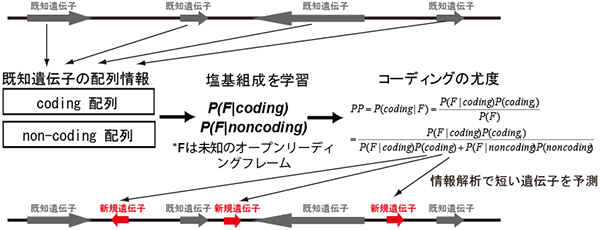
図1 情報解析を通じて既知遺伝子が存在しないところに短い遺伝子を予測する方法
既知のアミノ酸をコードする配列(coding配列)とそれ以外の配列(non-coding配列)を集めてきて、その塩基組成を学習させ、未知のオープンリーディングフレーム*のうち、coding配列のパターンに類似しているものを、新規遺伝子の候補として同定した。
*オープンリーディングフレーム:ペプチドあるいはタンパク質に翻訳される可能性があるDNA・RNA領域のこと
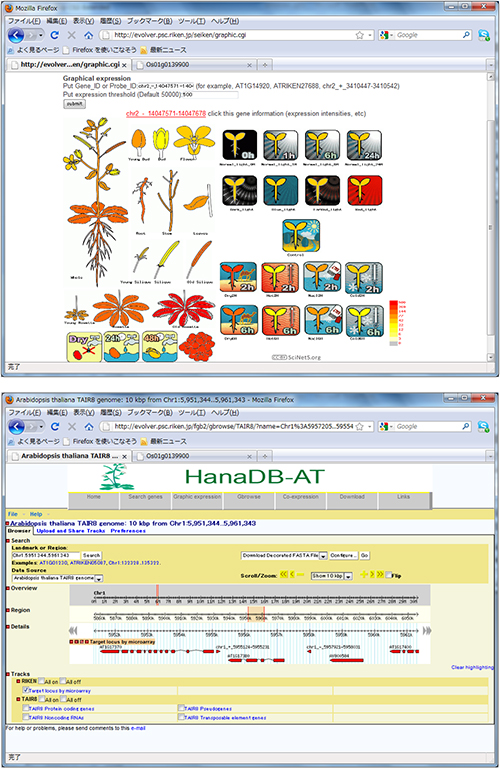
図2 上 新規に推定し短い遺伝子の33条件下のRNA発現(HanaDB-AT)
下 同定した短い遺伝子の位置(HanaDB-AT)
上:一番左が植物の全体図で、その隣に16カ所の組織を示している。右上が日射時間や光の種類による8つの異なる光条件、右下が乾燥、塩害などの植物に与える9つの異なるストレス条件。RNA発現の強度を色で表し、赤色ほど非常に強い発現、黄色になる程弱い発現を示す。
下:赤い部分が短い遺伝子の位置。
HanaDB-AT:HPで公開。
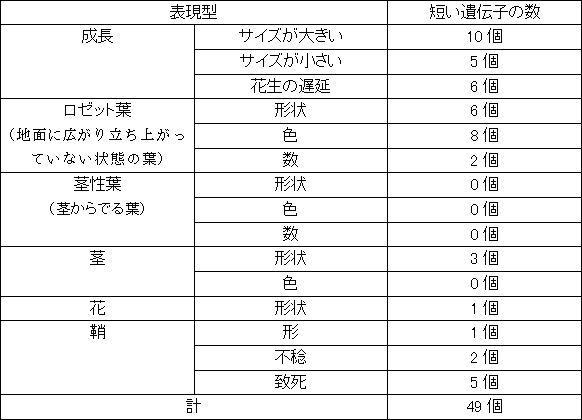
表1 短い遺伝子の過剰発現体が示す表現型のカテゴリー
ペプチドをコードする短い遺伝子の中から無作為に473個選び、それぞれの遺伝子がコードするペプチドを過剰発現する過剰発現体を作製した。その結果、49個の過剰発現体に形態異常が確認された。
